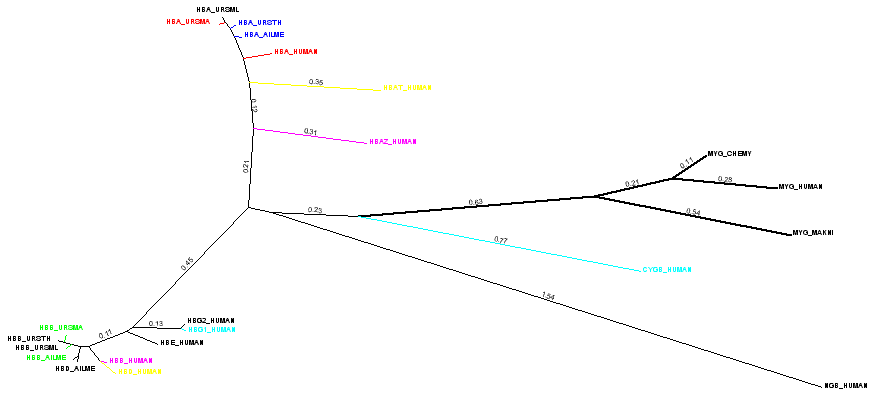
- Названия последовательностей из внешней группы выделены жирным шрифтом, соответствующие им ветви — наиболее толстые в дереве.
- Разные группы ортологов покрашены в
,
,
цвета.
- Разные группы паралогов покрашены в
,
,
цвета.
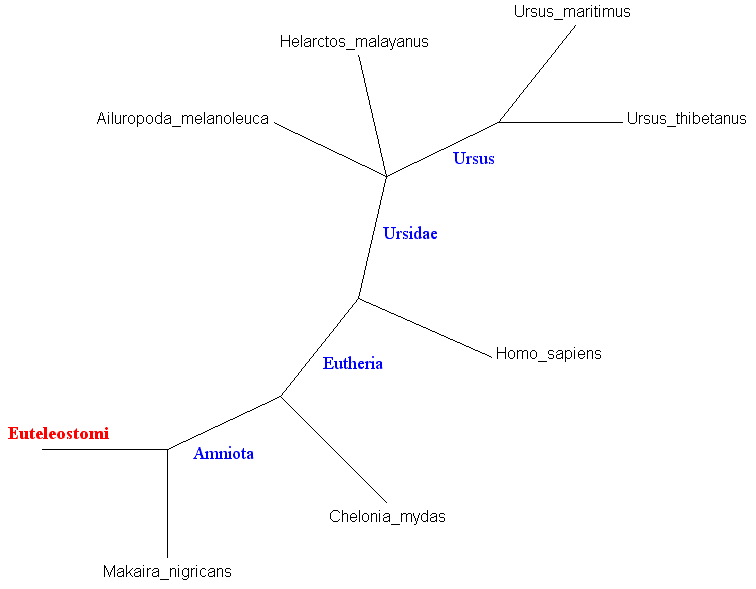
|
В начало страницы.
На главную страницу.