- Краткое описание структуры в файле 2cv0.pdb В файле приведены координаты атомов следующих молекул
- Глутамил-тРНК синтетаза
- тРНКн
Белок принадлежит - thermus thermophilus
Для исследования была выбрана
цепь D, представляющая глутамин-тРНК со следующей последовательностью:
[501] 5' - GGCCCCAUCGUCUAGCGGUUAGGACGCGGCCCUCUCAAGGCCGAAACGGGGGUUCGAUUCCCCCUGGGGUCACCA - 3' [576],
В последовательности на 3'-конце имеется триплет CCA, к которому присоединяется аминокислота. Координаты атомов приведены.
- Исследование вторичной структуры
С помощью программы find_pair пакета 3DNA были определены возможные водородные связи
между азотистыми основаниями (файл 2cv0.out).
В соответствии с полученными данными:
- акцепторный стебель состоит из участка 501-507 и комплементарного ему участка 566-572.
- Т-стебель состоит из участка 549-552 и комплементарного ему участка 562-565.
- D-стебель состоит из участка 510-513 и комплементарного ему участка 522-525.
- антикодоновый стебель состоит из участка 527-531 и комплементарного ему участка 539-543.
акцепторный стебель выделен красным, Т-стебель - зеленым, D-стебель - синим, антикодоновый - оранжевым.
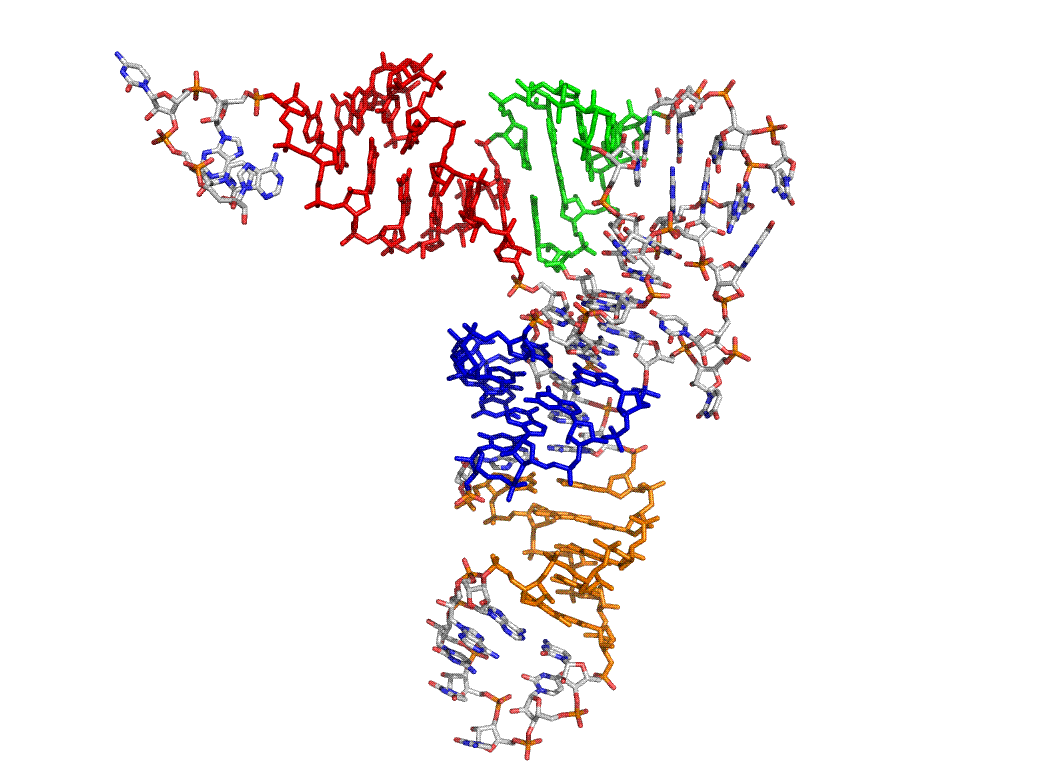
Рис.1. Вторичная структура глутамин-тРНК из 2cv0.pdb
|
PyMOL code
select anticodon, (i. 527) | (i. 528) | (i. 529) | (i. 530) | (i. 531) | (i. 531) | (i. 539) | (i. 540) | (i. 541) | (i. 542) | (i. 543)
select d-stem, (i. 510) | (i. 511) | (i. 512) | (i. 513) | (i. 522) | (i. 523) | (i. 524) | (i. 525)
select t-stem, (i. 549) | (i. 550) | (i. 551) | (i. 552) | (i. 562) | (i. 563) | (i. 564) | (i. 565)
select acseptor, (i. 501) | (i. 502) | (i. 503) | (i. 504) | (i. 505) | (i. 506) | (i. 507) | (i. 566) | (i. 567) | (i. 568) | (i. 569) | (i. 570) | (i. 571) | (i. 572)
color orange, anticodon
color blue, d-stem
color green, t-stem
color red, acseptor
hide
show sticks, br. (n. **')
|
Структуру стеблевых дуплексов поддерживают 18 канонических и 2 неканонических пар оснований.
Одна из неканонических пар:
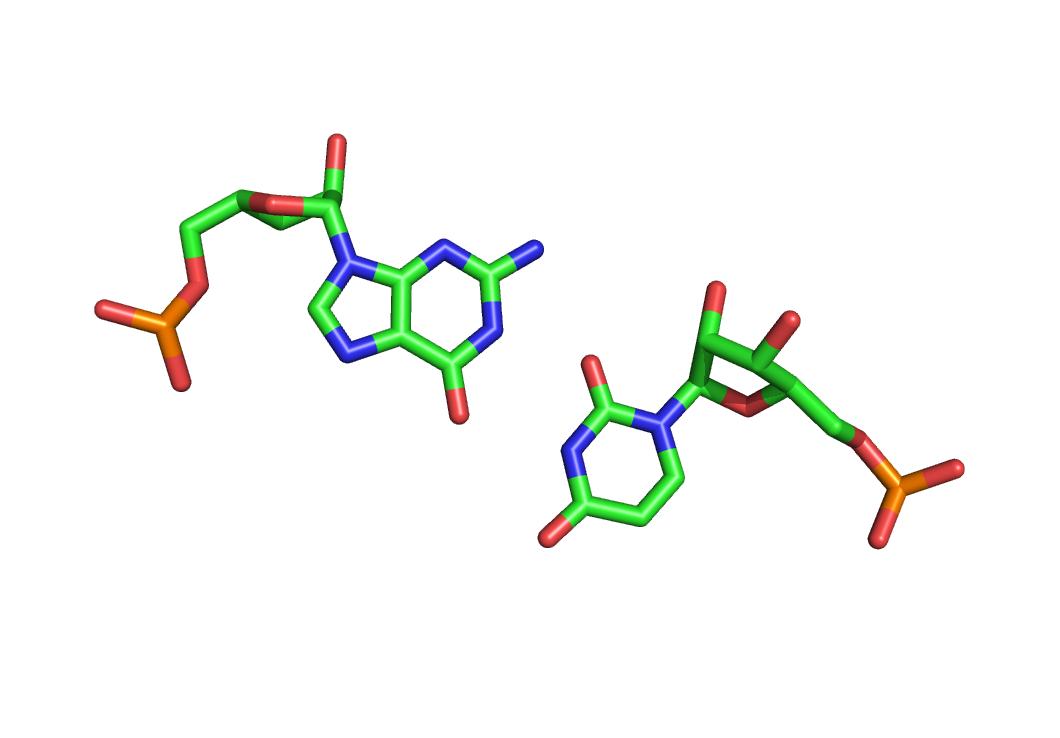
Остаток тимидина в Т-петле - отсутствует;
Дигидроуридины в D-петле - отсутствуют;
- Исследование третичной структуры
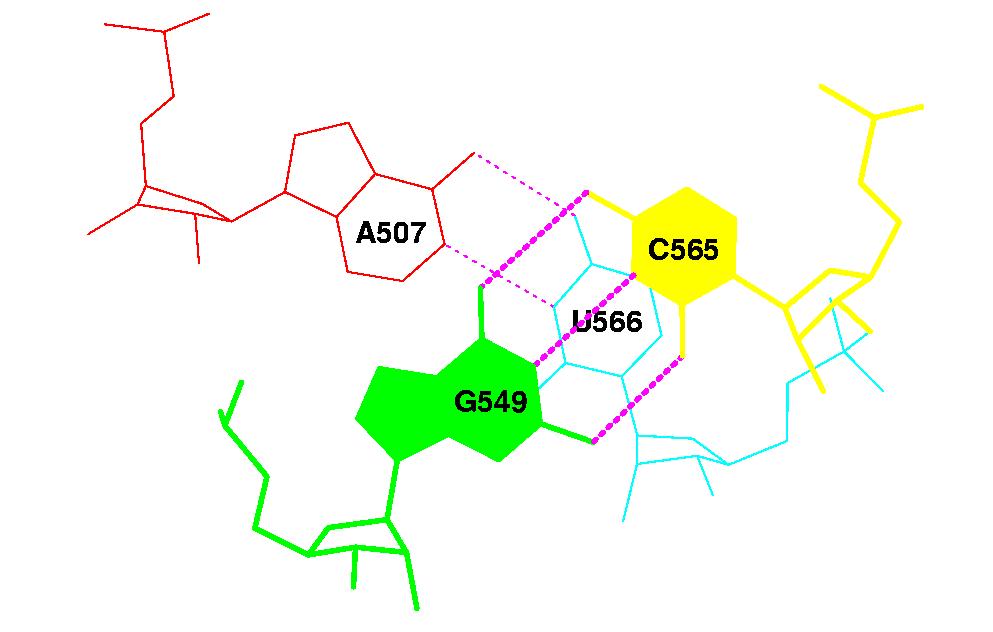
- Образование стекинга на конце акцепторного и начале Т-стебля сомнительно,
как показано на рисунке нуклеотиды практически не перекрываются:
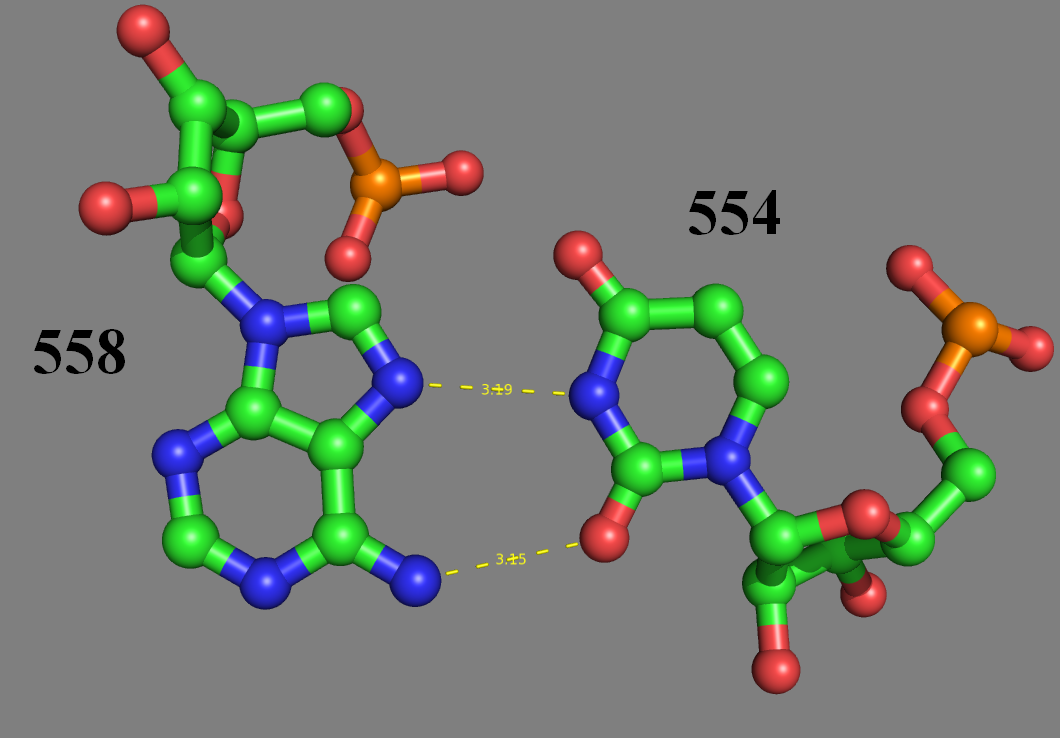
Имеются дополнительные водородные связи между основаниями D- и Т-петель:
554-558
555-518
514-508
515-548
519-556
количество канонических пар: 4
количество неканонических пар: 1
- Предсказание вторичной структуры тРНК
Реальная и предсказанная вторичная структура тРНК из файла 2cv0.pdb
| Участок структуры
|
Позиции в структуре
(по результатам find_pair)
|
Результаты предсказания
с помощью einverted
|
Результаты предсказания
по алгоритму Зукера
|
| Акцепторный стебель | 5' 501-507 3'
5' 566-572 3'
Всего 7 пар |
предсказано 6 пар из 7 реальных | предсказано 6 пар из 7 реальных |
| D-стебель | 5' 510-513 3'
5' 522-525 3'
Всего 4 пары |
предсказано 0 пар из 4 реальных | предсказано 5 пар из из которых 4 реальные |
| T-стебель | 5' 549-552 3'
5' 562-565 3'
Всего 4 пары |
предсказано 0 пар из 4 реальных | предсказано 0 пар из 4 реальных
(хотя отражено +/- положение стебля) |
| Антикодоновый стебель | 5' 527-531 3'
5' 539-543 3'
Всего 5 пар |
предсказано 5 пар из 5 реальных | предсказано 5 пар из 5 реальных |
| Общее число канонических пар нуклеотидов | 28 |
17 | 16 |
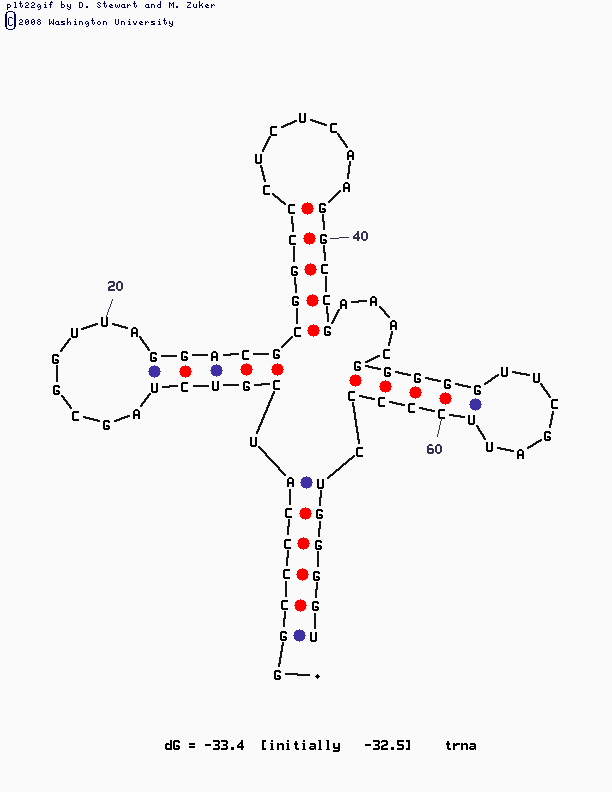
Структура РНК сначала предсказывалась с помощью программы einverted, наиболее похожий на реальность результат
программа выдала если этом штаф за гэп был установлен в 15, а параметр match в 10; остальное осталось по умолчанию
Потом использовался алгоритм Зукера, реализованный в программе mfold, использовались разные параметры, но
даже запуск программы по умолчанию дал наилучший вариант:
|
|
На главную
Третий семестр
|