В структуре присутствует ион двух валентного железа.

В записи 5RXN банка PDB представленно 3 треонина. Боковая цепь имеет зеркальную симметрию и по данной записи можно сказать, что треонин хирален.
Структура была расшифрованна в 1984 году. Разрешение 2 А. Информации о данных остатках в REMARK не найдено.
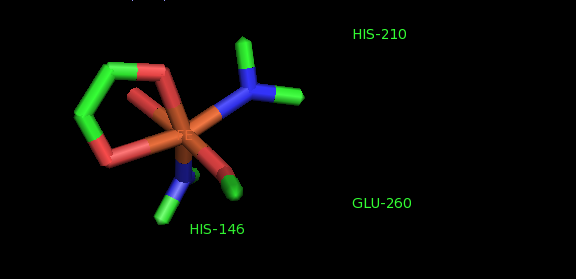
Остаток 167 цепи С - аргинин. Удивительно то, что в этом остатке есть ещё одна связь между N и C.
Остаток 136 цепи А - аспарагин. Также как и в ARG-167 есть связь между N и C, но ещё есть связи между OD1 и CB, ND2 и CB.
Возникнуть такое могло из-за того, что в программе установлено слишком большое расстояние между ядрами атомов, которое является критическим для прорисовки связи.
Структура была расшифрованна в 1999 году. Разрешение 3.30 А. Информации о данных остатках в REMARK была найдена следующая:
- REMARK 480 ZERO OCCUPANCY ATOM. THE LOCATION AND PROPERTIES OF THESE ATOMS MAY NOT BE RELIABLE - Нулевой занятости атом. Местоположение и свойства этих атомов могут не соответствовать реальности.
- REMARK 500 THE FOLLOWING ATOMS ARE IN CLOSE CONTACT. - Следующие атомы близко расположены (ARG-167 and ASP-169; ASP-97 and ASN-136)
- REMARK 500 THE FOLLOWING RESIDUES HAVE A PSEUDO PLANARITY TORSION - Следующие остатки имеют пcевдо плоскость: ASN-136 (10.49).

Все эти четыре остатка являются триптофанами. Но все они различаются по конформации. Кольца триптофана цепи А находятся почти на одной плоскости, в цепи B и С - также, а в цепи D кольца находятся почти под прямым углом друг к другу. При этом любое отличное от угла 180 между плоскостями колец является не верным изображением, так как эти кольца имеют ароматические свойства и должны находиться на прямой плоскости, но это в программе похоже не установлено.
Структура была расшифрованна в 1990 году. Разрешение 2.9 А. Информации о данных остатках в REMARK не найдено.

III. Cкрипт для PyMOL к последнему заданию с записью 7GPB.
cd H:\Term5\Practice1 |
IV. Впечатления от PyMOL. В чём он лучше RasMol, а в чём – хуже?
Первые впечатления от PyMol остались вполне положительные. Можно, зная команды, легко добиться того, что нужно. Рассмотреть молекулы/остатки со всех сторон. Получить необходимые изображения.
Единственное, смущает отсутствие подробного описания команд. Например, мне пришлось столкнуться с проблемой подписывания цепей - а именно командой label. Если с ней работать в визуальном окне, то проблем нет. Но при написании скрипта подписать должным образом цепи так и не удалось. Почему-то при вводе команды label (resi 67),chain цепи подписываются так, если нажать из визуального окна (sele) -> label -> chain identifier. Хотя удобнее, чтобы он подписал просто с помощью chains. Разобраться даже с помощью руководства не получилось.
С RasMol сравнивать не могу, т.к. также тесно ещё с ним не сталкивалась.