Гомологичное моделирование комплекса
белка с лигандом
-
Цель занятия ознакомится с возможностями гомологичного моделирования комплекса белка с лигандом.
В этом занятии мы будем пользоваться пакетом Modeller. Это программное обеспечение распространяется бесплатно для академических пользователей.
Работаем с белком лизоцимом из указанного организма. Используя известную структуру лизоцима форели как образец, необходимо построить модель комплекса нашего белка с лигандом.
Программе MODELLER для моделирования структуры белков, в качестве входных данных нужны: управляющий скрипт, файл pdb со структурой-образцом, файл выравнивания с дополнительной информацией.
-
Построим выравнивание последовательности из структуры ID: 1lmp и предложенного
нам белка ( LYSC_CERTO ).
Полученное выравнивание сохраняем в формате PIR. -
Модификация файла выравнивания:
Переименуем последовательность в файле выравнивания как в примере:
Было Стало >P1;uniprot|P37712|LYSC_CAMDR >P1;seq >P1;1LMP__|PDBID|CHAIN|SEQUENCE >P1;1lmp
После имени последовательности моделируемого белка добавим строчку:sequence:ХХХХХ::::::: 0.00: 0.00
Эта строчка описывает входные параметры последовательности для modeller.
После имени последовательности белка-образца добавим:structureX:1lmp_now.ent:1 :A: 132 :A:undefined:undefined:-1.00:-1.00
В конце каждой последовательности добавьте символы:/.
Символ "/" означает конец цепи белка. Точка указывает на то, что имеется один лиганд (если бы было два лиганда стояли бы две точки). -
Модификация файла со структурой: удалим всю воду из структуры (в текстовом редакторе)
всем атомам лиганда присвоим один и тот же номер "остатка" (MODELLER считает, что
один лиганд = один остаток) и модифицируем имена атомов каждого остатка, добавив в
конец буквы A, B, C. Смысл операции в том, что атомы остатка 130 имели индекс А,
атомы остатка 131 имели индекс В и т.д. . После модификации имен атомов изменим
номера остатков на 130.
Пример:
Было Стало HETATM 1014 O7 NAG 130 HETATM 1014 O7A NAG 130 HETATM 1015 C1 NAG 131 HETATM 1015 C1B NAG 130
Результат: 1lmp_now.ent -
Создание управляющего скрипта my_seq.py (my_seq - имя Вашей последовательности, например, lysc_chram)
Заготовка:
from modeller.automodel import * class mymodel(automodel): def special_restraints(self, aln): rsr = self.restraints for ids in (('OD1:98:A', 'O6A:131:A'), ('N:65:A', 'O7B:132:A'), ('OD2:73:A', 'O1C:133:A')): atoms = [self.atoms[i] for i in ids] rsr.add(forms.upper_bound(group=physical.upper_distance, feature=features.distance(*atoms), mean=3.5, stdev=0.1)) env = environ() env.io.hetatm = True a = mymodel(env, alnfile='test1.ali', knowns=('1lmp'), sequence='seq') a.starting_model = 1 a.ending_model = 5 a.make()В скрипте указано:
- что нужно использовать стандартные валентные углы в полипептидной цепи (строчка 4)
- что дополнительно нужно сохранять взаимное расположение определенных пар атомов (3.5 ангстрема); В данном случае трех атомов белка, образующих водородные связи с тремя атомами лиганда - строчки 5-7 с ID пар атомов; параметры взаимного расположения атомов пары описаны в строчке 9-10. 3 точки могут однозначно расположить сложную структуру в пространстве, поэтому мы выбираем водородные связи как источник данных точек.
- что ковалентные связи в гетероатомах нужно вычислять по расстояниям между атомами (так же, как это делает Rasmol), строчка 12
- что имя файла с выравниванием и имена последовательностей образца и моделируемого белка, строчка 13 (а имя файла со структурой содержится в выравнивании)
- что число и номера моделей, которые нужно построить (в данном примере 5 моделей), строки 14-15
- что пора строить модель строчка 16
В скрипте Вам необходимо отредактировать строчки, в которых указаны какие водородные связи белка с лигандом должны быть в будущей модели. Критерий водородной связи: расстояние менее 3.5 ангстрем между азотом или кислородом белка с подходящими атомами лиганда.
Получаем скрипт. -
Запустим скрипт командой:
mod9v7 myscript &
Получаем следующие файлы:
file1.pdb
file2.pdb
file3.pdb
file4.pdb
file5.pdb
Попробуем наложить структуры друг на друга: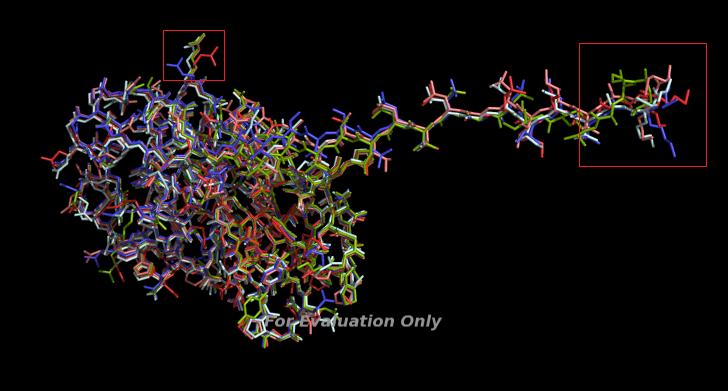
Полученные модели весьма схожи и хорошо накладываются, однако в выделенных областях структуры различны. - Попробуем выбрать наилучшую модель из вышепредставленных.
Инструменты для оценки качества структуры можно найти в веб интерфейсе WHATIF.
Воспользуемся следующими:
Ramachandran plot evaluation,
Anomalous bond lengths,
Coarse Packing Quality Control.
1 2 3 4 5 Ramachandran Z-score 0.127 0.143 0.094 -0.725 -0.195 RMS Z-score for bond angles 1.055 0.930 0.918 0.940 0.919 Average for range -1.605 -1.537 -1.527 -1.624 -1.549
Проанализировав получившиеся структуры, можно сказать, что все модели построены относительно неплохо; тем не менее, 3-я модель чуть лучше остальных.
© Азнаурян 2008 marina-91@list.ru