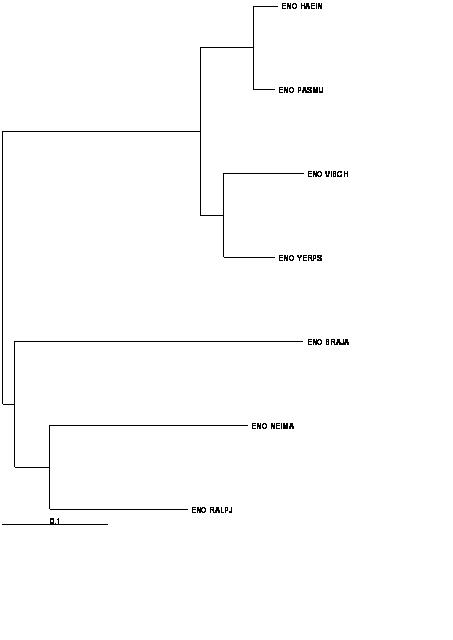
В предыдущем задании (задания 1 и 2) были построены филогенетические деревья
выбранных семи бактерий. Невозможно укоренить дерево, построенное методом максимальной бережливости, потому что
он не предполагает различия в расстояниях между листьями (не предполагает молекулярных часов),
и fneighbor с алгоритмом UPGMA, так как оно уже укоренено.
В предыдущем задании дерево было построено алгоритмом Neighbor-joining:
+----------ENO_NEIMA
+-1
! +-------ENO_RALPJ
!
! +ENO_HAEIN
! +--3
! ! +ENO_PASMU
2-----------4
! ! +----ENO_VIBCH
! +-5
! +--ENO_YERPS
!
+---------------ENO_BRAJA
Полученную формулу:
(((ENO_HAEIN:0.02338,ENO_PASMU:0.02066):0.04994,(ENO_VIBCH:0.07559,
ENO_YERPS:0.04895):0.02194):0.18703,(ENO_BRAJA:0.27318,(ENO_NEIMA:0.18782,
ENO_RALPJ:0.1305):0.03317):0.01138);
откроем программой TreeView и получим изображение:

г====3:ENO HAEIN
г=========11
¦ L====4:ENO PASMU
г=========================================10
¦ ¦ г================5:ENO VIBCH
¦ L===12
=13 L==========6:ENO YERPS
¦
¦ г=============================================================7:ENO BRAJA
L==8
¦ г==========================================1:ENO NEIMA
L======9
L=============================2:ENO RALPJ
Укоренение прошло в ветвь 2-4 (см. дерево, построенное Neighbor-joining).
Полученное дерево имеет такие же нетривиальные ветви, как и правильное дерево.
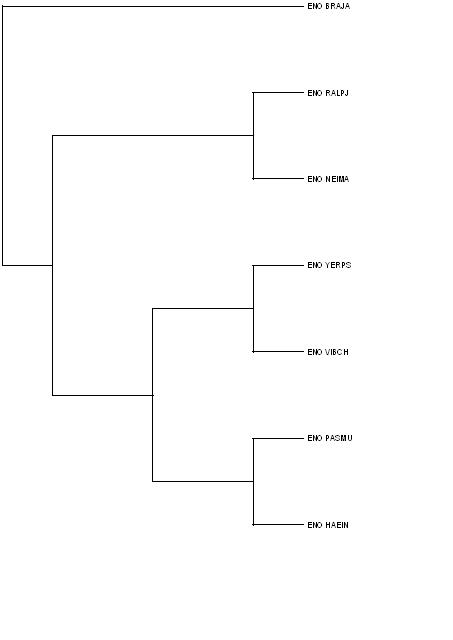
Реконструируем дерево по семейству белков энолаз, в качестве аутгруппы используем ENO_BACSU (Bacillus subtilis).
Fprotpars выдала следующий результат:
+--ENO_RALPJ
+--------------7
! +--ENO_NEIMA
!
! +--ENO_YERPS
+--6 +-----5
! ! ! +--ENO_VIBCH
! ! +--4
! ! ! ! +--ENO_PASMU
1 +-----2 +-----3
! ! +--ENO_HAEIN
! !
! +-----------ENO_BACSU
!
+--------------------ENO_BRAJA
После обработки и укоренения дерева программой retree и выделения аутгруппы получили следующее:
г>>>>>>>>>>>>>>>>>>>>7:ENO BACSU
¦
¦ г>>>>>8:ENO BRAJA
==9 г>>>>>>>>>>10
¦ ¦ ¦ г>>1:ENO RALPJ
¦ ¦ L>11
¦ ¦ L>>2:ENO NEIMA
L>12
¦ г>>3:ENO YERPS
¦ г>>>>14
¦ ¦ L>>4:ENO VIBCH
L>>>>>>>13
¦ г>>5:ENO PASMU
L>>>>15
L>>6:ENO HAEIN
С помощью программы fseqboot было создано 100 бутстрэп-реплик выравнивания белков выбранных бактерий,
с помощью fprotpars по полученным репликам были составлены деревья, из которых по принципу "расширенного большинства"
было создано единое дерево, совпавшее с правильным:
+------ENO YERPS
+-54.2-|
| +------ENO VIBCH
+-100.0-|
| | +------ENO HAEIN
+-60.6-| +-100.0-|
| | +------ENO PASMU
+------| |
| | +--------------------ENO BRAJA
| |
| +---------------------------ENO NEIMA
|
+----------------------------------ENO RALPJ
4 ветви не получили поддержку: