Подготовим файл координат и файл топологии. В прошлом занятии был предоставлен gro файл с 38 молекулами этана. Создадим индекс файл в котором будет группа из одной молекулы этана.
make_ndx -f box_38.gro -o 1.ndx
Выбераем остаток номер 1. Появиляется новая группа.
Теперь создадим gro файл с одной молекулой и зададим ячейку . При запуске editconf выбераем номер, соответствующей группе из одной молекулы.editconf -f box_38.gro -o et1.gro -n 1.ndx #зададим ячейку и расположим молекулу по центру ячейку editconf -f et1.gro -o et.gro -d 2 -c
э Получили файл et.gro. Исправим файл топологии et.top из прошлого задания. В разделе [ molecules ] изменим количество молекул этана с 38 на 1.Даны 5 файлов с разными параметрами контроля температуры:
be.mdp - метод Берендсена для контроля температуры.
vr.mdp - метод "Velocity rescale" для контроля температуры.
nh.mdp - метод Нуза-Хувера для контроля температуры.
an.mdp - метод Андерсена для контроля температуры.
sd.mdp - метод стохастической молекулярной динамики.
Напишем скрипт для работы с 5ю системами.
Создаём отдельную папку для каждого метода.
mkdir ${i} # где i: be,vr,nh,an,sdСначала надо построить входные файлы для молекулярно-динамического движка mdrun с помощью grompp:grompp -f mdp/${i}.mdp -c et.gro -p et.top -o ${i}/et_${i}.tprДолжно получиться 5 tpr файлов. Теперь для каждого из них запустим mdrun.
mdrun_d -deffnm ${i}/et_${i} -v -nt 1Теперь переходим к анализу результатов. Начнем с визуального анализа. Для каждой из 5 систем проведите конвертацию в pdb и просмотрите в PyMol.
trjconv -f ${i}/et_${i}.trr -s ${i}/et_${i}.tpr -o ${i}/et_${i}.pdbПолученные ролики для PyMOL:et_an.pdb et_be.pdb et_nh.pdb et_sd.pdb et_vr.pdb - Некоторые наблюдения:
- В методе Андерсена видны небольшие небольшие колебания по длинам связей и валентным углам и совершенно нет вращения. Такое состояние, наверное, характерно для низких температур, то есть для кристалла.
- В методе Берендсена вначале видны всевозможные амплитудные колебания и вращения, но постепенно молекула начинает всё больше вращаться, а амплитуда колебаний уменьшается. Это выглядит совсем нереалистично.
- В методе Нуза-Хувера движение кажется реалистичным. Небольшие колебания и вращение. Молекула в основном находится в заторможенной конформации, довольно часто видна и заслонённая.
- В методе стохастической молекулярной динамике молекула очень быстро меняет своё положение. Похоже на вращение, но трудно проследить какое-то направление, будто она случайным образом меняет свою ориентацию или сталкивается с другими молекулами.
- Метод "Velocity rescale" похож на метод Нуза-Хувера. Отличие в том, что здесь более амплитудные колебания и меньше вращения по связи. Конформации, близкие к заслонённой, прослеживаются редко.
Сравним потенциальную энергию связи и кинетическую энергию для каждой из 5 систем.
echo -e "Bond\nKinetic-En.\n0" | g_energy -f ${i}/et_${i}.edr -o ${i}/et_${i}_en.xvg > ${i}/et_${i}.txtПостроим графики изменения энергий.
Создадим файлы скриптов для Gnuplot и выполним их (сохраним графики в формате PNG):echo "set datafile commentschars '#@&' set term 'png' set output '${i}/en_${i}.png' set pointsize 0.5 plot '${i}/et_${i}_en.xvg' using 1:2, '${i}/et_${i}_en.xvg' using 1:3 " > ${i}/gnu_${i}.gnu #запуск gnuplot cat ${i}/gnu_${i}.gnu | gnuplotРассмотрим распределение длинны связи С-С за время моделирования. Сначала создадим индекс файл с одной связью. В текстовом редакторе создаём файл b.ndx со следующим содержимым:
[ b ] 1 2
И запустим утилиту по анализу связей g_bond:g_bond -f ${i}/et_${i}.trr -s ${i}/et_${i}.tpr -o ${i}/bond_${i}.xvg -n b.ndxПостроим графики распределения длинн связей. Сделаем отображение в Gnuplot в виде boxes.
echo "set datafile commentschars '#@&' set term 'png' set output '${i}/bond_${i}.png' plot '${i}/bond_${i}.xvg'with boxes " > ${i}/gnu_bond_${i}.gnu cat ${i}/gnu_bond_${i}.gnu | gnuplot\Создадим список наших изображений и после работы цикла сольём их в одно.ls -r ${i}/*.png >> image.list ... montage +frame +shadow +label -tile 2x5 -geometry 640x480 `cat image.list` images.pngПолученные изображения - слева энергия для каждого состояния (красным цветом потенциальная энергия связей, зелёным - кинетическая энергия), справа распределения длин связей.
AN BE NH SD VR 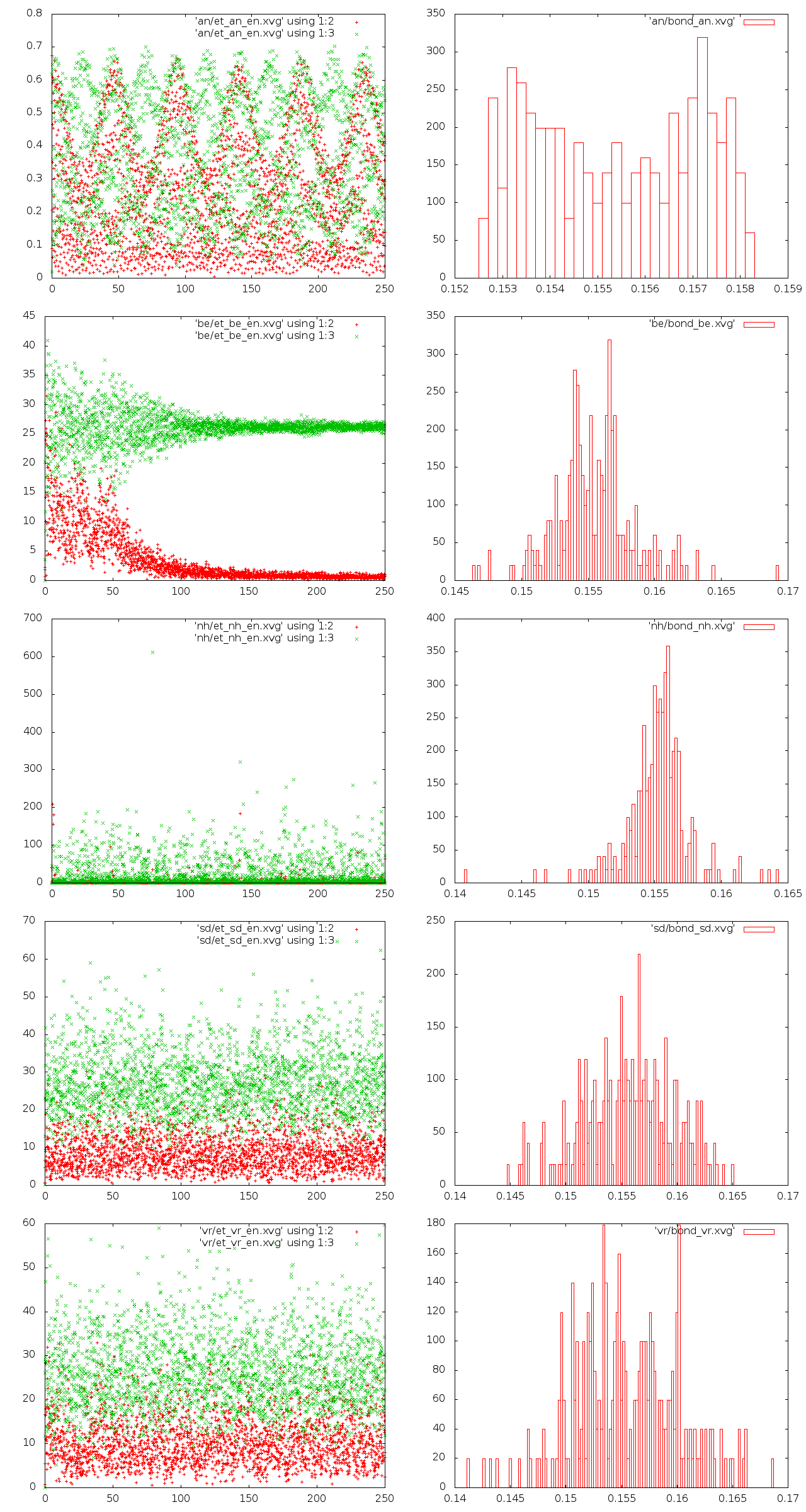
Распределение Максвелла-Больцмана имеет следующую форму:
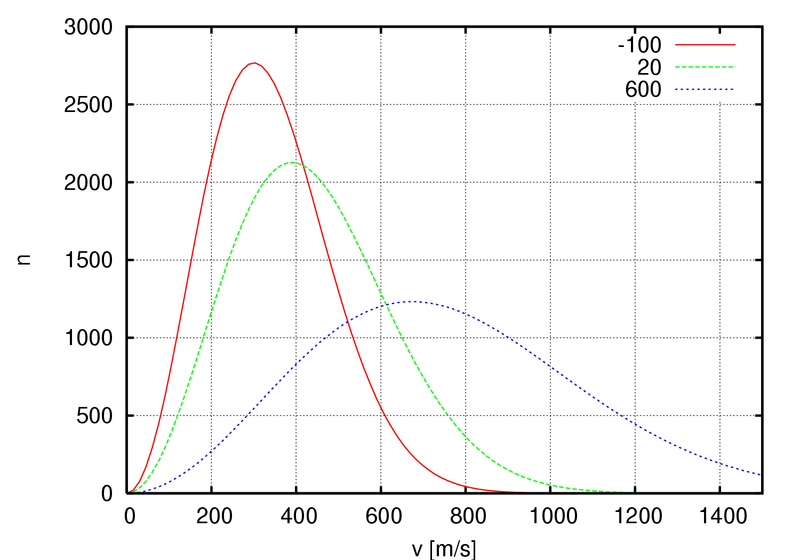
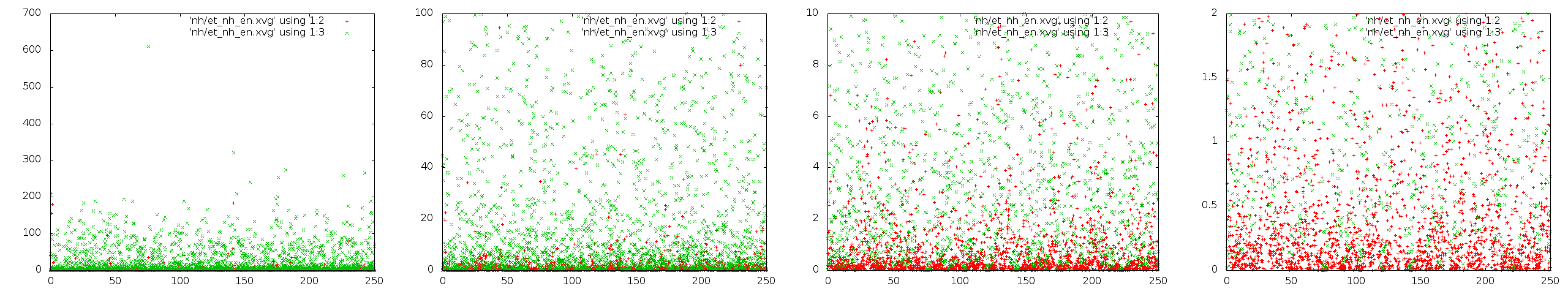
Ему совершенно не соответствуют графики методов Андерсена и Берендсена, неплохо соответствуют графики методов стохастической молекулярной динамики и "Velocity rescale". Метода Нуза-Хувера нуждается в дополнительной проверке. Для этого было сделано ещё несколько графиков в другом масштабе.
Что ж, чёткий пик плотности в небольшом отдалении от нуля не наблюдается, распределению Максвелла-Больцмана не соответствует.
Исходя из всех наблюдений, можно сказать, что реалистичны 2 метода: стохастической молекулярной динамики и "Velocity rescale". Но на роликах в PyMOL первый кажется немного странным, поэтому более реалистичен, наверное, метод "Velocity rescale".