Исходное дерево.
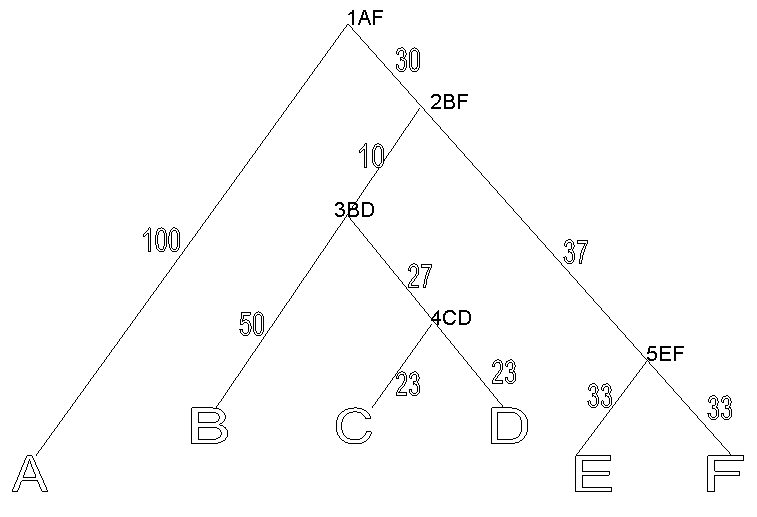
На главную страницу
Реконструкция филогенетического дерева с помощью 4-х разных методов.
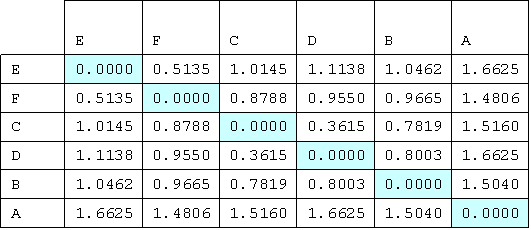
Были определены эволюционные расстояния по Джуксу - Кантору между последовательностями выравнивания(состоящего из последовательностей листьев) с помощью программы ednadist, для параметра "Transition/transversion ratio" было использовано значение 1.0, поскольку в эволюционной модели транзиции и трансверсии не различались.
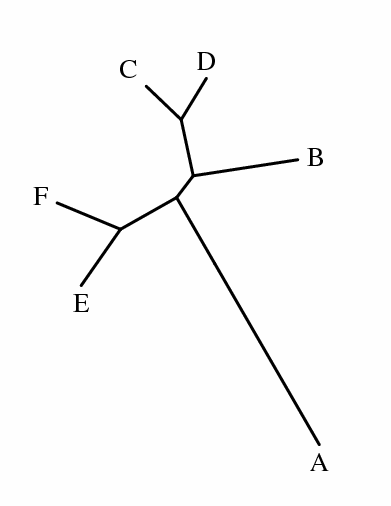
Далее приведены филогенетические деревья,
построенные по следующим методам и их скобочные формулы:
+--------------E
+--------------2
! +--------------F
+----------------4
! ! +----------C
! ! +------------1
--5 +-----3 +----------D
! !
! +-----------------------B
!
+----------------------------------------------A
| 
|
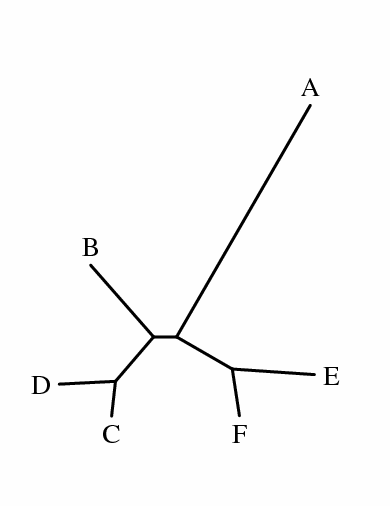
(((E:0.25675,F:0.25675):0.24115,((C:0.18075,D:0.18075):0.21480, B:0.39555):0.10235):0.28466,A:0.78256);
|
+----C
+------2
+--3 +------D
! !
! +-----------B
!
--4-------------------------------A
!
! +---------E
+-------1
+-----F
|
|
(((C:0.13864,D:0.22286):0.23216,B:0.37819):0.09121,A:1.05987,(E:0.32626, F:0.18724):0.25493);
|
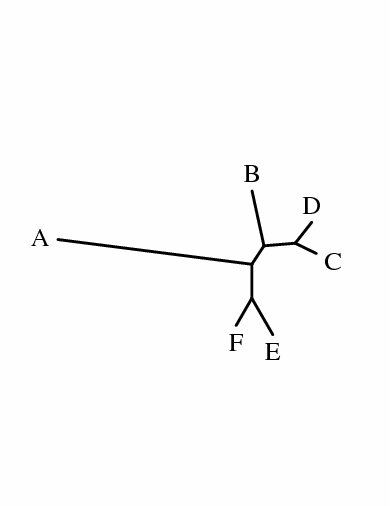
+-------F ! ! +----------------------------------------------A --1-------4 ! ! +------------B ! +-----3 ! ! +------D ! +------2 ! +-----C ! +---------E |
|
(F:0.24729,(A:1.54385,(B:0.44295,(D:0.21033,C:0.18506):0.24796):0.17437):0.26891, E:0.33107);
|
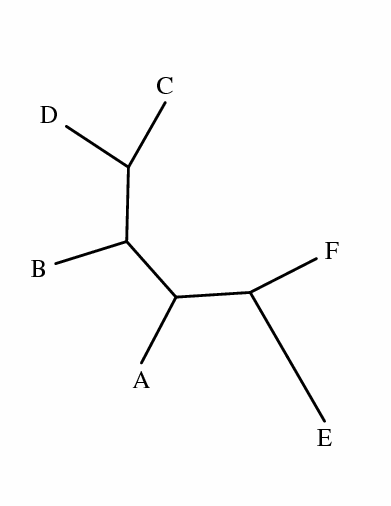
+--------A
+--5
! ! +-----B
! +--4
+--2 ! +--D
! ! +--3
! ! +--C
--1 !
! +-----------F
!
+--------------E
| 
|
(((A,(B,(D,C))),F),E);
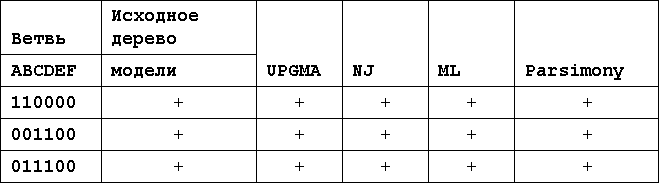
Далее приведена оцененка того, насколько реконструируется исходная топология филогенетического дерева. Cравнение топологии исходного филогенетического дерева модели и 4-х вариантов его реконструкции Для этого описана топология полученных деревьев в следующей таблице:
Реконструкция хода эволюции при такого уровня расстояниях между последовательностями не очень надежна, так как все, использованные методы дают более менее хорошие результаты при "хороших" данных, когда расстояние ветвей примерно 20 н.о.
Все методы строят исходное дерево. Но у всех метобов соотношения длин ветвей получилось разным. Наидолее правдоподобным, по соотношению длинн ветвей(так как все остальные параметры у всех оказальсь примерно одинаковыми, за исключением метода UGPMA, который основан на принципе биологических часов и, соответственно, построил ультраметрическое, укорененное дерево), мне показался метод Parsimony (метод максимальной экономии). Этот метод построил дерево которое, если укоренить в точке 1, будет ультраметрическим и совпадают соотношения ветвей В,С и D. Но при этом не совпадает длинны ветвей А и Е. С этой точки зрения еще лучшим методом представляется UGPMA, но я думаю, что если бы сое дерево не было бы практически ультраметрическим, то результат UGPMA был бы хуже по сравнению с другими.
Алгоритмы UPGMA и Neighbor-Joining используют матрицу попарного расстояния, а Maximum Likelihood и Parsimony являются символьно-ориентировонными.